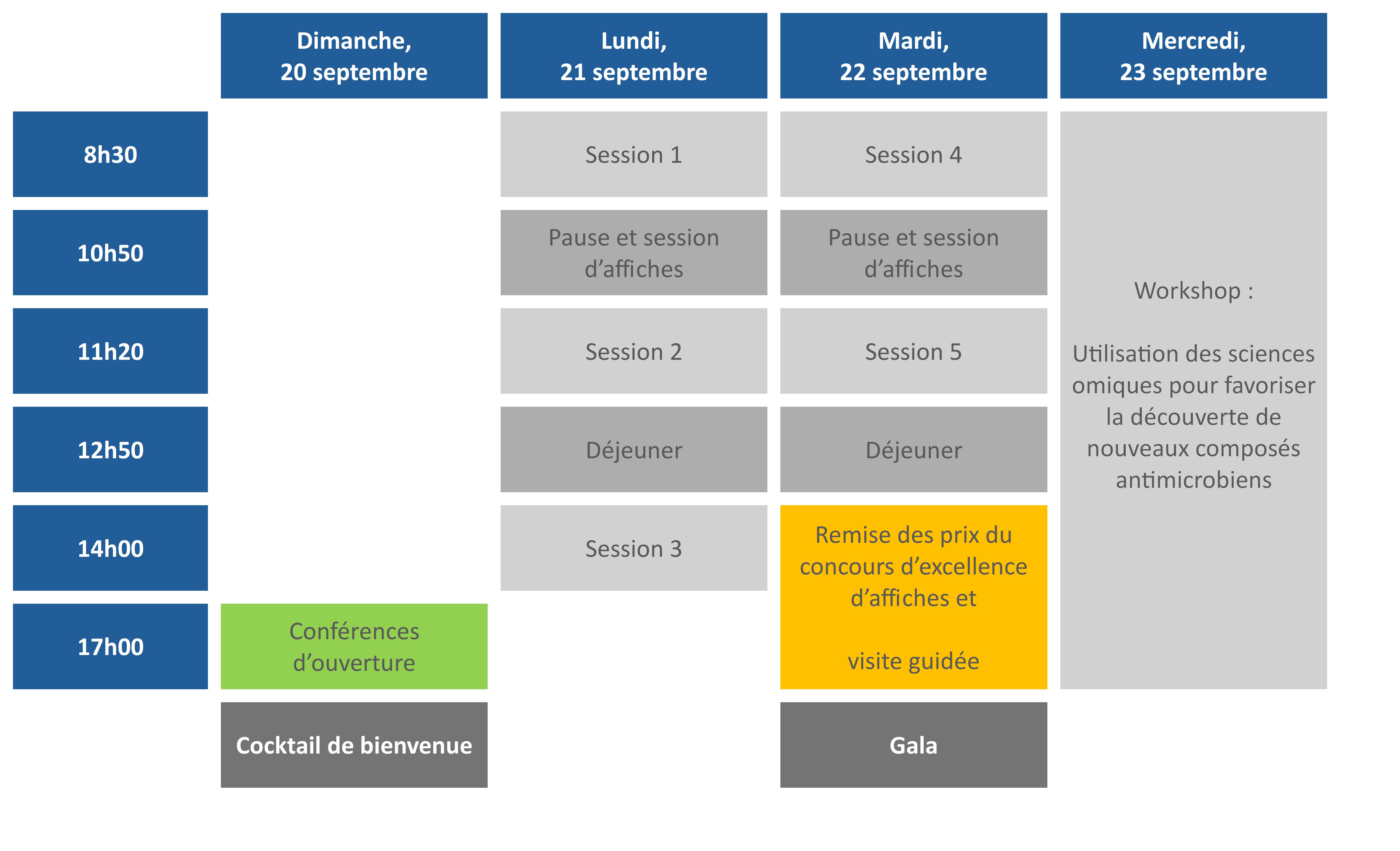
Programme préliminaire
17h00 - 20h00
- Cesar de la Fuente, University of Pennsylvania, Philadelphie, États-Unis
Accelerating antibiotic discovery with AI
Résumé
- Sylvie Rebuffat, Muséum national d'Histoire naturelle, Paris, France
The continuous story of bacteriocins until emerging origins and methods for discovery
Résumé
8h30 - 17h30
- Laurent Bazinet, Université Laval, Québec, Canada
Combining statistical, machine learning and experimental approaches for screening of novel antimicrobial peptides from complex hydrolysates
Résumé
- Éric Biron, Université Laval, Québec, Canada
The lipopeptide brevibacillin: A promising scaffold for the development of antimicrobials with tunable pharmacological properties and spectra of activity
Résumé
- Frédéric Borges, Université de Lorraine, Nancy, France
Top-down strategies for engineering microbial communities with antimicrobial properties
Résumé
- Françoise Coucheney, Université de Lille, Villeneuve d'Ascq, France
Bacteriocins from Lacticaseibacillus paracasei CNCM I-5369: anti-Escherichia coli activity, original export system, potential medical application
Résumé
- Véronique Delcenserie, Université de Liège, Liège, Belgique
Dynamic gastrointestinal models as engineering tools to decipher food-microbiome-probiotic interactions
Résumé
- Séverine Zirah,Muséum national d'Histoire naturelle, Paris, France
Microcin diversity and role in competitive interactions in poultry microbiota
Résumé
8h30 - 22h00
Ismail Fliss, Université Laval, Québec, Canada
Résumé
Simon Heilbronner, Ludwig-Maximilians-Universität München, Planegg-Martinsried, Allemagne
Feast or Famine: Nutrient Sharing Affects S. aureus Growth in the Nasal Ecosystem
Résumé
Sunday Ochai, International Center for Antimicrobial Resistance solutions, Copenhague, Danemark
AMR in a Changing Environment: Bridging Evidence, Policy, and practice Gaps at the Climate-AMR Nexus in Low- and Middle-Income Countries
Résumé
8h30 - 16h30
Workshop: Approches intégratives et intelligence artificielle pour la recherche d'antimicrobiens
Animatrice: Séverine Zirah, Muséum national d'Histoire naturelle, Paris, France
Cet atelier proposera une expérience immersive conçue pour familiariser les participants avec la diversité des ensembles de données « omiques » ainsi qu’avec les principes de classification et d’apprentissage automatique appliqués à la recherche sur les antimicrobiens.
Après une introduction aux méthodes multi-omiques ainsi qu'aux méthodes de classification et d'apprentissage automatique, un atelier pratique sur ordinateur utilisera un ensemble de données compilé à partir d'une collection de souches d'Enterobacteriaceae résistantes aux antibiotiques (1,2). L'analyse conjointe des données phénotypiques (activités antimicrobiennes des bactériocines) et des données génomiques visera à générer des outils permettant de prédire la sensibilité des souches aux bactériocines, suivie d'une évaluation de leur pertinence.
Références:
1. Telhig S, Pham NP, Ben Said L, Rebuffat S, Ouellette M, Zirah S, Fliss I. Exploring the genetic basis of natural resistance to microcins. Microb Genom. 2024,10:001156. doi: 10.1099/mgen.0.001156.
2. Telhig S, Ben Said L, Torres C, Rebuffat S, Zirah S, Fliss I. Evaluating the Potential and Synergetic Effects of Microcins against Multidrug-Resistant Enterobacteriaceae. Microbiol Spectr. 2022, 10:e0275221. doi: 10.1128/spectrum.02752-21.
Aperçu du programme